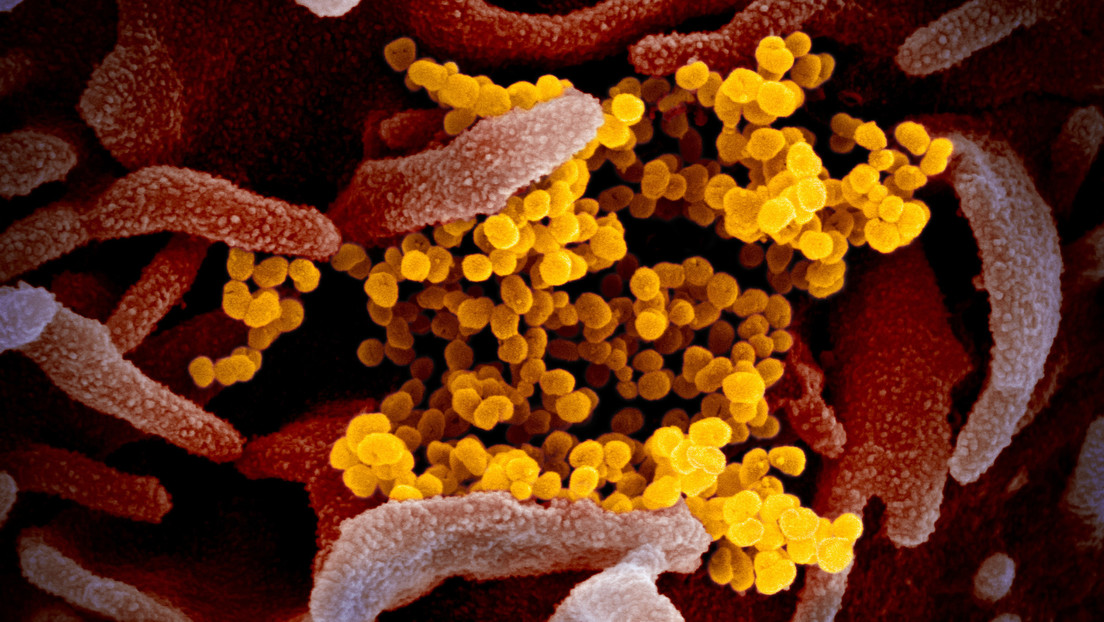
Científicos completan simulaciones masivas del coronavirus en un superordenador para ayudar a crear vacunas
Un grupo de científicos ha completado las simulaciones masivas del nuevo coronavirus, que ya se ha cobrado la vida de más de 27.000 personas e infectado a casi 600.000 a nivel mundial, según recoge el portal ScienceDaily.
Los investigadores están preparando el modelo informático completo de todos los átomos de la envoltura del SARS-CoV-2, es decir, el componente exterior del coronavirus. Ya probaron las primeras partes del modelo y optimizaron el código en el superordenador Frontera en la Universidad de Texas, en EE.UU. Científicos completan simulaciones masivas del coronavirus en un superordenador para ayudar a crear vacunas
Un grupo de científicos ha completado las simulaciones masivas del nuevo coronavirus, que ya se ha cobrado la vida de más de 27.000 personas e infectado a casi 600.000 a nivel mundial, según recoge el portal ScienceDaily.
Los investigadores están preparando el modelo informático completo de todos los átomos de la envoltura del SARS-CoV-2, es decir, el componente exterior del coronavirus. Ya probaron las primeras partes del modelo y optimizaron el código en el superordenador Frontera en la Universidad de Texas, en EE.UU. Esto puede ayudar a crear medicamentos y vacunas para combatir el mortífero virus que provoca el covid-19.
La autora principal del estudio y profesora de química y bioquímica en la Universidad de California, Rommie Amaro, explicó que de momento su grupo intenta «combinar datos en diferentes resoluciones en un modelo cohesivo que pueda simularse» en las instalaciones como el Frontera. Se estima que en total este modelo contendrá aproximadamente 200 millones de átomos.
«Si tenemos un buen modelo de cuál es el aspecto exterior de la partícula y cómo se comporta, obtendremos una buena visión de los diferentes componentes que están involucrados en el reconocimiento molecular», es decir, cómo el virus interactúa con los receptores de la célula huésped, señaló Amaro.
Del 12 al 13 de marzo su laboratorio realizó simulaciones de dinámica molecular en hasta 4.000 nodos, o alrededor de 250.000 núcleos de procesamiento.Esto puede ayudar a crear medicamentos y vacunas para combatir el mortífero virus que provoca el covid-19.
La autora principal del estudio y profesora de química y bioquímica en la Universidad de California, Rommie Amaro, explicó que de momento su grupo intenta «combinar datos en diferentes resoluciones en un modelo cohesivo que pueda simularse» en las instalaciones como el Frontera. Se estima que en total este modelo contendrá aproximadamente 200 millones de átomos.
«Si tenemos un buen modelo de cuál es el aspecto exterior de la partícula y cómo se comporta, obtendremos una buena visión de los diferentes componentes que están involucrados en el reconocimiento molecular», es decir, cómo el virus interactúa con los receptores de la célula huésped, señaló Amaro.
Del 12 al 13 de marzo su laboratorio realizó simulaciones de dinámica molecular en hasta 4.000 nodos, o alrededor de 250.000 núcleos de procesamiento.